Collection of ITS2 region reference sequences for freshwater fish in the Japanese archipelago for environmental DNA metabarcoding applications
https://mbmg.pensoft.net/article/162895/list/1/
環境DNAメタバーコーディングでは、採水した水に含まれるDNA断片をまとめて調べることで、その場所にいる生物を推定できます。魚類の調査では、これまでミトコンドリアDNAの12S rRNA領域を対象にした MiFish が広く使われてきました。感度が高く、多くの研究で実績がある一方で、近縁種を種レベルまできれいに見分けにくいことがある、という課題があります。
今回取り上げる論文は、その弱点を補う候補として、核DNAの ITS2 領域 に注目した研究です。
著者らは、日本列島の淡水魚、とくに琵琶湖水系の魚類を対象にITS2用プライマーを設計し、参照配列ライブラリを整備しました。そのうえで、ITS2がMiFishよりもどの程度、種の違いを見分けやすいのかを比較しています。論文の要点は、ITS2がすべての魚にとって万能なマーカーというより、MiFishでは識別が難しいいくつかの分類群を補完できる可能性が高い という点にあります。
はじめに
淡水生態系は、人為的な環境改変や気候変動の影響を受けやすく、そこに生息する淡水魚の保全は急ぎの課題になっています。ですが、川や湖の魚を正確に調べるには、場所ごとに異なる採集道具や手法が必要で、広い範囲を短時間で把握するのは簡単ではありません。こうした背景から、水中に残されたDNAを調べる環境DNAが、魚類の分布把握に有効な手段として注目されてきました。
環境DNAメタバーコーディングの利点は、1つの水試料から複数種を同時に検出できることです。従来法では網や罠、目視などを組み合わせても取りこぼしが生じますが、環境DNAでは対象生物を直接捕獲しなくてもよいため、希少種や警戒心の強い種の検出にも向いています。魚類分野では、MiFishプライマーによる12S rRNA領域の増幅が標準的な方法になっており、海域、河川、湖沼など多くの環境で使われてきました。
ただし、MiFishにも限界があります。ミトコンドリアDNAは1細胞あたりのコピー数が多いため環境DNA解析と相性がよい一方で、近縁種間では配列差が小さく、種レベルまで区別しにくい場合があります。また、ミトコンドリアDNAは母系遺伝なので、雑種の検出には不利です。魚類の保全や分布評価では、属レベルの情報ではなく、種の情報を知りたい場面が多いため分解能は重要です。
そこで候補になるのが核DNAです。核DNAは一般には1細胞あたりのコピー数が少ないため、環境DNAの標的としては不利とされてきました。しかし、リボソームDNA (rDNA) は核DNAの中で繰り返し配列として多数存在し、さらに種間差が比較的大きい領域を含みます。
ITS領域はその代表例で、コイやオオサンショウウオでは、ミトコンドリアDNAより高感度に検出できたという先行研究も紹介されています。つまり、ITSは核DNAで不利とされた欠点を解消し、対象によっては高い感度と高い識別力を両立できる可能性がある領域と言えます。
ただし、魚類ではITS領域の分子系統学的利用がそれほど進んでおらず、地域ごとに十分整備された参照データベースもありません。環境DNAメタバーコーディングは、得られた配列を照合する相手、つまり参照配列がなければ種名を割当られません。
そのため、新しいマーカーを使う場合は、まずどの種にどの配列が対応するのかを、地域の魚類相に即して整理する必要があります。著者らはこの点を重視し、まず琵琶湖水系をモデル地域としてITS2参照配列の整備に取り組みました。琵琶湖は日本列島でも淡水魚多様性が高く、魚類相がよく調べられており、MiFish参照データベースも利用しやすいため、新しい核DNAマーカーを試す場として適しています。
この研究の目的は以下の3つです。
- 魚類用ITS2メタバーコーディングプライマーを設計すること
- 琵琶湖水系の淡水魚を中心としたITS2参照配列を収集すること
- ITS2とMiFishの種識別能を比較し、ITS2がどの分類群で有効なのかを明らかにすること
上記を踏まえて、論文の解説を進めていきます。
メソッド
ITS2プライマーの設計
著者らは、魚類の核rRNA遺伝子のうち、ITS2を挟む5.8S領域から28S領域の配列をNCBIから収集し、MUSCLEでアライメントを行いました。
アラインメントとは
複数の配列を並べて、どの位置が保存され、どこに違いがあるかを見やすくする処理です
その結果をもとに、多くの魚種で共通して保存されている場所にプライマーを手動で設計しました。フォワード側は113種、リバース側は96種の配列を参考にして、ソフトウェア任せではなく、分類群全体を俯瞰して保存的な領域を選定しています。
設計されたプライマー配列は以下の通りです。
- Forward:
Fish_ITS2_F: 5’-CYACGCCTGTCTGAGGGTC-3’ - Reverse:
Fish_ITS2_R: 5’-TCTCGTCTGATCTGAGGTCG-3’
フォワードプライマーの2文字目に入っている Y は、IUPAC表記でCまたはTを意味します。複数の塩基を許容することで、多くの魚種に対応しやすくしています。
論文では、このプライマーと既知配列のミスマッチ数も整理しており、Forward側では19塩基中10か所、Reverse側では20塩基中6か所で不一致が見られましたが、大部分は少数種に限られ、特にリバース側では各位置の不一致種数は2〜6種程度でした。さらに、組織由来DNAを用いたPCR確認では、琵琶湖に生息する12種すべてで増幅バンドが確認されました。つまり、少なくとも組織レベルでは、設計したプライマーは幅広い魚種に対して機能する と判断できます。
表1. 設計したITS2プライマーと各塩基位置における魚類配列とのミスマッチ数
Forward Primer
5'- C Y A C G C C T G T C T G A G G G T C -3' C 112 20 1 113 107 111 1 112 2 113 G 112 1 113 112 113 111 113 A 1 112 1 1 2 1 113 T 93 6 113 110 1 113 113 Reverse Primer
5'- T C T C G T C T G A T C T G A G G T C G -3' C 93 94 6 92 3 94 96 G 96 96 96 96 96 96 A 96 96 T 96 3 96 2 96 4 96 93 2 96 96
サンプル収集
参照配列の対象種は、主として『The Fishes of Lake Biwa』に基づいて選定されました。琵琶湖の魚類だけでなく、湖の下流にあたる淀川水系に分布するボラ Mugil cephalus とスズキ Lateolabrax japonicus も加え、合計84種が対象になっています。試料は琵琶湖・淀川水系を中心に採集され、一部の外来種などについては岐阜県や神奈川県など、別地域の標本も使用されています。
採集には投網やタモ網を用い、さらに琵琶湖博物館や研究者からの提供、観賞魚店や漁協からの入手も利用されました。希少種や保護対象種では、博物館所蔵標本も活用されています。
ライブラリ調製からシーケンス
DNAは各魚種の組織片または腹鰭から抽出され、一次PCRでは本研究で設計したITS2プライマーを使用しました。1st PCRの後、ExoSAP-ITで精製し、2nd PCRでMiSeqアダプターとインデックスを付加しています。その後、2nd PCR産物をまとめ、AMPure XPで精製したのち、Illumina MiSeqの2×300bp ペアエンドで配列決定を行っています。
インデックスとは
複数試料をまとめてシーケンスしても、後でどの試料由来かを区別できるようにする識別子配列です
MiSeqによるペアエンドシーケンスにて得られたFastqファイルは、DADA2を中心としたパイプラインで処理されました。具体的には、まずプライマー配列を除去し、次にASVを推定し、最後にフォワードとリバースリードを結合しています。
ASVとは
Amplicon Sequence Variant の略で、誤差補正後に得られるできるだけ実際の配列変異に近い単位です。OTUのようにまとめてクラスタリングする方法よりも、細かな配列差を保持しやすいのが特徴です。
種同定の際には、他の目の魚に80%以上一致するASVを候補から除外し、複数ASVが少数塩基差で並んだ場合には、シーケンスエラーの可能性を考えて最もリード数の多いものを残しています。また、2種についてはSanger法でも配列決定が行われました。
種の分解能評の価法
ITS2とMiFishの比較では、とくに識別が困難な4属、Oncorhynchus、Rhinogobius、Cobitis、Carassius に注目しています。これらはMiFishで近縁種が十分に分かれないことが知られているグループです。著者らは、各属内でBLASTによる相同性%を求め、その値をもとに種の分解能を4区分で評価しました。
| カテゴリ | 説明 |
|---|---|
| Easily distinguishable species | 種間一致率が98.5%以下で、しかもMiFishより低く、よりはっきり区別しやすい種 |
| Distinguishable species | 種間一致率が98.5%以下で、MiFishと同程度に区別できる種 |
| Difficult-to-distinguish species | 種間一致率が98.5%以上、または種内変異と種間差が大きく重なって区別しづらい種 |
| Indistinguishable species | 異種なのに配列が完全一致し、区別できない種 |
なお、今回評価した4属以外の魚については、ML法による系統樹が作成され、種間差が系統的に確認されています。
リザルト
プライマー設計と増幅の基本情報
設計されたITS2プライマーの増幅配列長は、対象分類群によって異なり、最長はオオクチバス属の Micropterus nigricans で481 bp、最短はカムルチー Channa argus で298 bpでした。組織由来DNAを用いたPCRでは、検証対象の12種すべてで増幅が確認されています。つまり、ITS2領域は分類群ごとに長さの変動があるものの、少なくとも今回の設計では多様な魚種のDNAを安定して増幅できると言えます。
参照配列の取得状況
2回のMiSeqランから得られた総リード数は 12,651,181 リード でした。対象とした84種のうち、本研究で新たにITS2配列を取得できたのは61種、リード数は291,855 リードです。さらに、今回の解析では取得できなかったものの、既存研究から利用可能な2種の配列を加えることで、最終的に63種分のITS2参照配列 が揃いました。これは対象84種の75%に相当します。配列が得られなかった21種の内訳は、試料未入手が3種、シーケンス品質不良が18種でした。
Oncorhynchus では ITS2 がとくに有効だった
まず注目されるのがサケ科 Oncorhynchus の結果です。琵琶湖水系に分布するビワマス Oncorhynchus biwaensis、アマゴ O. masou ishikawae、ニジマス O. mykiss の3種で比較したところ、ビワマスはITS2では他2種より 1.9~2.8%低い一致率 を示し、MiFishよりも明確に区別できました。このため、ビワマスは “easily distinguishable species” と判定されています。一方、アマゴとニジマスの関係は、ITS2でも98.5%以下ではあるものの、MiFishと比べて大きな改善ではなく、“distinguishable species” とされています。
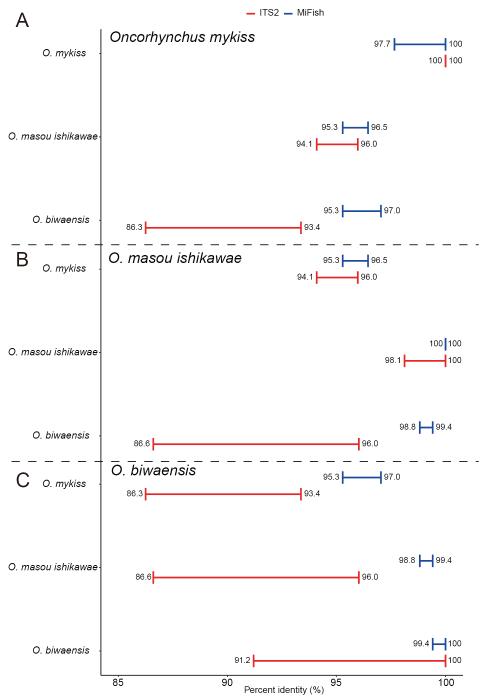
ただし、論文では注意点として、ビワマスの1配列では、種内変異が他種との種間差に重なるようなパターンが確認されています。解析個体数が2個体と少ないため、本当は種内多型が大きいのか、それともシーケンスエラーなのかは判断できていません。つまり、今回の結果は有望ですが、個体数を増やした検証 が必要です。
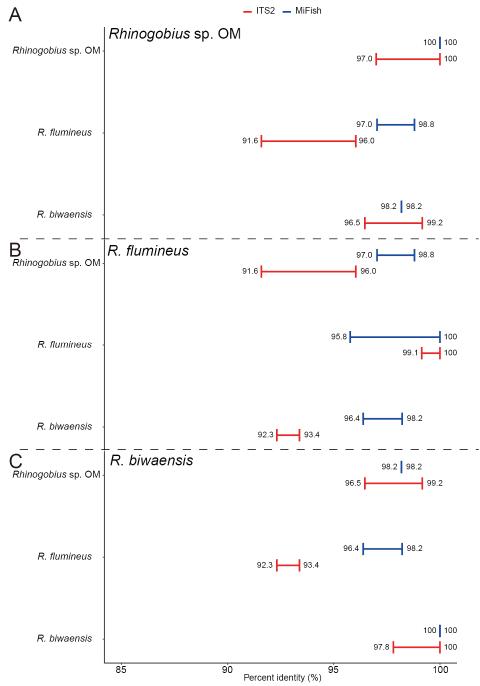
RhinogobiusでもITS2の改善が確認された
次にヨシノボリ属 Rhinogobius です。Rhinogobius sp. OM、ビワヨシノボリ R. biwaensis、カワヨシノボリ R. flumineus の3種を比較すると、カワヨシノボリはITS2で他2種より 1.0~3.0% 低い一致率 を示し、“easily distinguishable species” と判定されました。一方で、Rhinogobius sp. OM と R. biwaensis の間では一致率が99.5%以上で、種内変異とも大きく重なり、ITS2でも区別が困難なままでした。
この結果は、近縁種群の中でも、系統的に早く分岐した種ではITS2の効果が出やすいことを示唆しています。後の考察でも触れられていますが、R. flumineus は他の2種より古い時期に分岐したとされており、その分ITS2にも変異が蓄積していたと考えられます。
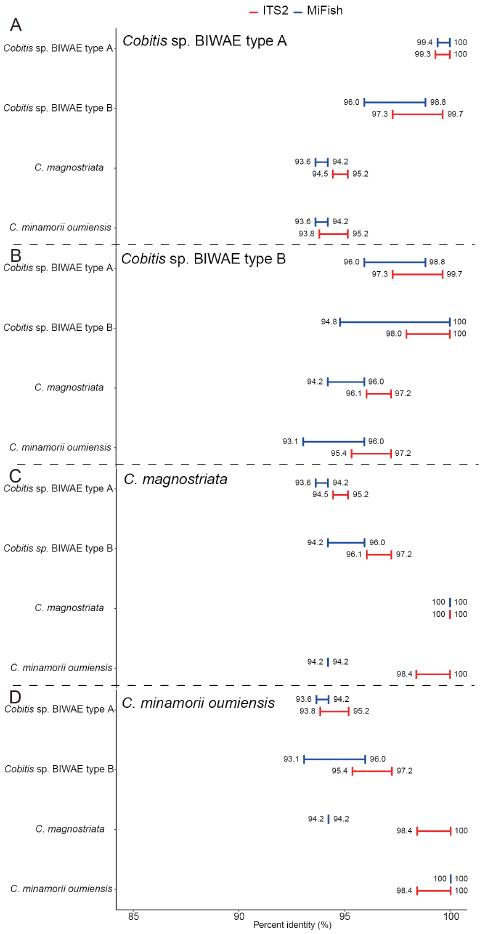
Cobitisは種ごとに異なる結果
シマドジョウ属 Cobitis は、ITS2の限界も含めて理解しやすい例と言えます。琵琶湖水系の4分類群、Cobitis sp. BIWAE type A、Cobitis sp. BIWAE type B、C. magnostriata、C. minamorii oumiensis を比較したところ、C. magnostriata と C. minamorii oumiensis は ITS2配列が完全一致 し、“indistinguishable species” になりました。
また、BIWAE type A と BIWAE type B も99.5%以上の高い一致率を示し、“difficult-to-distinguish species” と判定されています。一方、BIWAE type A/B と C. magnostriata または C. m. oumiensis の組み合わせは98.5%以下で、MiFishと同程度に区別できました。
つまり、Cobitisでは すべてを区別可能ではないが、一部の組み合わせでは使える という結果です。ITS2はMiFishを全面的に置き換えるものではなく、分類群ごとに得意不得意があることが、このあたりから分かります。
CarassiusではITS2の限界が目立った
フナ属 Carassius では、ITS2はあまり良い成績を示していません。Carassius sp. と C. buergeri grandoculis はITS2で完全一致となり、“indistinguishable species” に分類されました。さらに、C. cuvieri とそれら2分類群との間も98.5%以上で、結果として “difficult-to-distinguish species” と評価されています。MiFishでは少なくとも C. cuvieri を分けやすいとされる場面があるため、このグループではITS2の優位性が確認されませんでした。
この結果は、ITS2が万能ではないことをよく示しています。核DNAだから常に近縁種を分けやすいわけではなく、分類群によっては進化速度や交雑の歴史の影響で、むしろ差が出にくいこともあり得ます。

ディスカッション
ITS2はMiFish を置き換えるのではなく補完する
この論文の結論を簡潔にまとめると、ITS2は MiFishの代替ではなく補完マーカー です。実際、ビワマスやカワヨシノボリのように、MiFishでは識別が難しい、あるいは自信を持って種名を付けにくい分類群に対して、ITS2はより高い解像度を示しました。特にビワマスでの改善は、琵琶湖の重要種を対象とするモニタリングにとって意味が大きく、環境DNAを用いた分布把握や資源管理に新しい選択肢を与える結果といえます。
一方で、Cobitis や Carassius の一部ではITS2でも種分類できず、場合によってはMiFishのほうが結果が良い分類群もありました。論文でも、C. magnostriata と C. m. oumiensis、そして C. cuvieri・Carassius sp.・C. b. grandoculis では、MiFishのほうが優れた識別能を示すことがありました。
種レベルに分類出来ない理由には生物学的な背景がある
ITS2で区別できなかった種について、著者らは進化史や交雑の影響を議論しています。たとえば C. magnostriata は少なくとも3系統を起源にもつ異質四倍体種で、C. minamorii と複数の核DNA領域を共有するとされています。そのため、核DNA由来のITS2でも区別できなかった可能性があります。Carassius sp. と C. buergeri grandoculis の関係でも、三倍体の単為生殖系統と二倍体系統の間で交雑や遺伝子流動が起きており、その遺伝的均質性がITS2の差の小ささにつながったと解釈されています。
特定領域の配列が種ごとに分かれないからといって、必ずしも手法が悪いわけではありません。対象生物の進化史そのものが、そもそも単一マーカーでの識別に向いていない ことがあります。とくに倍数化、交雑、遺伝子流動のある群では、核DNAとミトコンドリアDNAで見え方が変わることも珍しくありません。
ITS2が有効だった種にも、まだ検証課題は残る
ITS2で改善が見られたOncorhynchusやRhinogobiusについても、議論の余地はあり、ビワマスでは解析個体数が少なく、種内多型の大きさがまだ十分に評価されていません。また、琵琶湖ではビワマスと導入されたアマゴの交雑が知られており、同所的な場所で両種のDNAが検出されたとしても、それが雑種由来かどうかを現在の環境DNAだけで厳密に判断するのは難しいと論文では述べられています。環境DNAで雑種を議論するには、理想的には単一細胞レベルに近い情報が必要になるからです。
Rhinogobius についても、R. flumineus が分けやすかった一方、Rhinogobius sp. OM と R. biwaensis はITS2でもほぼ分かれませんでした。両者は浅い分岐時期と複雑な交雑歴が示唆されており、その遺伝的近さがITS2にも表れていると考えられています。環境DNAで種判定を行うときには、こうした分類群ごとの遺伝的事情 を踏まえて、どこまでを種判定とし、どこからは属や種群として扱うかを決める必要があります。
リファレンスデータベースの拡張が今後の鍵
今回、最終的に63種分のITS2参照配列が揃ったことは大きな成果ですが、未整備の分類群も残っています。論文では、ウナギ科、ボティア科、メダカ科、カダヤシ科、ケツギョ科、タウナギ科など、琵琶湖で1種しか確認されていない科は、近縁種の参照配列が不足しており、環境DNAによる確実な種同定が難しいことが指摘されています。今後はこうした未収集の種を優先的に補うことが重要です。
また、14種については近縁種の配列が既に存在し、系統関係からある程度の推定ができる可能性があるとされており、なかでも Acheilognathus、Biwia yodoensis、Hemibarbus labeo、Squalidus japonicus japonicus、Silurus lithophilus、Gymnogobius isaza などは、MiFishで区別が困難な種を含むため、ITS2で追加的な利点が出るかどうかは今後の焦点になります。
環境DNA調査ではマルチマーカーによる評価が必要
論文の結論でも強調されているように、魚類多様性をできるだけ正確に捉えるには、今回の例だとITS2とMiFishを組み合わせるのが現実的です。MiFishは感度と既存の知見の多さに強みがあり、ITS2は一部の近縁種群で高い識別力を発揮します。両者の併用は、「MiFishでは属止まりだがITS2なら種まで分類可能な群」と、「ITS2では分類が困難だがMiFishでは比較的分類が可能な群」の両方をカバーしやすくなります。著者らは今後、琵琶湖水系の実際の環境DNAサンプルでITS2メタバーコーディングを検証し、さらに参照データベースを拡張していく必要があると述べています。
免責事項
十分注意は払っていますが、本記事の情報・内容について保証されるものではありません。また、本記事の利用や閲覧によって生じたいかなる障害についても責任を負いません。そして、本記事の情報は予告なく変更される場合がありますので、ご理解くださいますようにお願い申し上げます。