水生昆虫における環境DNAメタバーコーディング: mtDNA 16S領域に基づくMtInsects-16SプライマーセットとmtDNA COI領域に基づく汎用マーカーの比較
水生昆虫の環境DNAメタバーコーディングにおいて、mtDNA 16S rRNA領域の MtInsects-16S と mtDNA COI 領域の一般マーカーを比較し、検出性能と参照DBの重要性を評価した論文です。
水生昆虫は分類群が広く、種同定の難易度も高いため、どのマーカーを使うかと参照DBの整備が検出結果を大きく左右します。本稿では、実河川での環境DNA解析と採集を突き合わせた点に注目しながら解説します。
- 掲載誌: Environmental DNA (Wiley) / オンライン公開: 2024-07-18
- DOI: 10.1002/edn3.588
- 対象河川: 相模川水系・酒匂川水系(神奈川県)
- 調査設計: 6地点 x 各3繰り返し
- 比較プライマー: MtInsects-16S (16S rRNA) / COI一般マーカー(fwhF2 + EPTDr2n)
- 参照DB: 神奈川県の水生昆虫参照配列を整備
プライマー開発論文の解説記事はこちら。
Abstract
長期的な生物多様性モニタリングのために、水生昆虫の環境DNA調査は簡便で有効な手法です。しかし、mtDNA COI 領域を用いた従来研究では、分類群の網羅性が不十分で、藻類・珪藻など非標的生物の増幅が頻発することが課題とされてきました。さらに、水生昆虫の参照配列がデータベースに少ない点も問題でした。
本研究では、以前に開発された mtDNA 16S rRNA 領域の新規プライマー MtInsects-16S を用い、神奈川県の水生昆虫に関する参照DBを整備したうえで、2河川水系6地点(各3繰り返し)の環境DNAメタバーコーディングを実施しました。mtDNA COI 領域の一般マーカーと16S領域の結果を比較し、同地点での採集調査の種リストと照合して検出性能を評価しています。
採集で得られた種リストに対して、MtInsects-16S は 74.9% を検出し、COI一般マーカーは 40.1% を検出しました。両プライマーの併用では 80.0% を検出しています。参照DBの整備を前提とすれば、MtInsects-16S による水生昆虫の環境DNA解析は高い精度と信頼性を持つことが示され、16S領域は水生昆虫環境DNAに不可欠なマーカーであると結論づけられています。
Keywords: eDNA, aquatic insects, metabarcoding, mtDNA 16S rRNA, COI, primer, reference database
背景
水生昆虫の環境DNA解析では、これまでmtDNA COI 領域が広く用いられてきました。COI はバーコーディングの標準領域として実績がありますが、水生昆虫に限って見るとプライマーの汎用性が十分でないことが報告されており、非標的生物の増幅が起きやすい点も課題でした。結果として、特定の分類群が検出されにくかったり、リードの多くが目的外の配列に消費されることがあります。
一方、16S rRNA領域は保存性の高い部位と可変領域がバランスよく配置されており、広い分類群に安定して増幅できるプライマー設計が可能です。MtInsects-16S は水生昆虫に特化した16Sプライマーとして開発されており、今回の研究は「16Sのメリットが実河川データでどこまで示せるか」を検証した位置づけにあります。
さらに重要なのが参照DBの整備です。環境DNAメタバーコーディングは、シーケンスされた配列を参照DBに照合して同定するため、参照DBが薄い分類群は検出率が下がるという構造的な弱点があります。
本研究では神奈川県内の水生昆虫の参照配列を集約し、地域特化のDBを構築したうえで解析を行っています。これは「プライマー性能」と「DB品質」を同時に押し上げた設計であり、現場で再現性のある検出を目指すうえで示唆に富むアプローチです。
この論文の位置づけ
MtInsects-16Sは、以前の研究で設計・提案された水生昆虫向けの16Sプライマーです。
本論文はその「実地検証編」にあたり、実河川での環境DNA分析と採集を並行して行うことで、プライマーの有効性と参照DBの重要性を定量的に示しています。
開発→実装→検証の流れが明確な点が、本研究の価値を高めています。
研究目的と問い
この研究の問いは次の2点です。
- MtInsects-16S は COI 一般マーカーに比べて、水生昆虫をより高い割合で検出できるか
- 参照DBを整備した条件下で、環境DNAの検出結果が採集とどの程度整合するか
つまり、 「マーカーの比較」 と 「DB整備の実効性」 を同時に検証する実験設計になっています。単に環境DNAの検出種数を出すのではなく、採集データを基準に評価している点が重要です。
調査地と採水設計
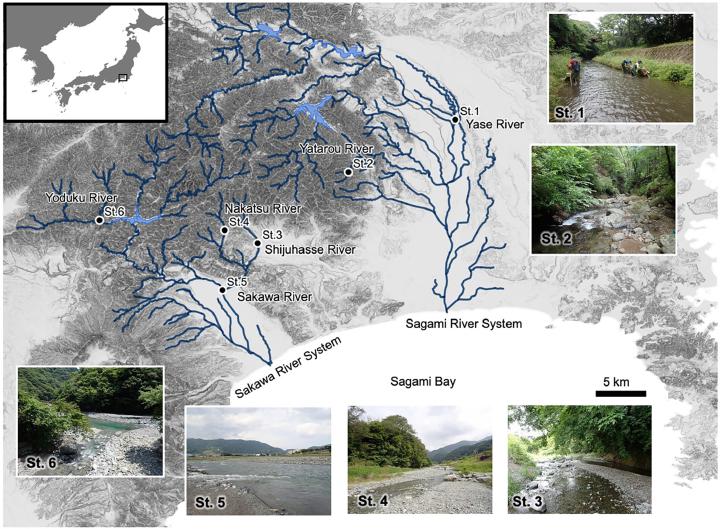
調査は神奈川県内の2河川水系で実施され、相模川水系の4地点と酒匂川水系の2地点から採水されています(Fig. 1)。図中には各地点の写真も示され、河道の規模や周辺植生が異なることがわかります。これにより、同じ県内でも異なる環境条件を反映したデータが得られる設計になっています。
Methods
参照DB構築
神奈川県内の水生昆虫(主にカゲロウ目・カワゲラ目・トビケラ目)を対象に、相模川・酒匂川で2020〜2021年に採集した標本を河川水辺の国勢調査の手順(NCRE: National Census on River Environments)で同定し、参照DBを構築しています。
COI の一般バーコード領域 (LCO1490/HCO2198) のうち fwhF2 + EPTDr2n が狙う短領域と、MtInsects-16S を含む AQdb16S (長断片) を解析対象に設定し、全長mtDNAのショットガン (ペアエンド150 bp) と2-step tailed PCRによるターゲット増幅 (MiSeq 2×300 bp) を併用して配列を取得しました。得られた配列は県の環境DNA DBと GenBank を併用して解析に利用されます。
捕獲調査
物理採集は2021年5月24~26日に実施され、NCREの手順に沿って定量・定性の両方を行っています。定量調査では、各サイトの瀬に 0.25 m × 0.25 m の方形区を3つ設置し、サーバーネット (開口250 mm、メッシュ0.493 mm: NGG38) で採集しました。定性調査は3名で Dフレームネットを使い、瀬・淵・ワンドなどの微小生息場を広くカバーするように採集しています。
環境DNA調査(採水・保存・ろ過・抽出)
採水は各地点で1 Lの表層水をポリプロピレンボトルで採取し、 捕獲調査の前に実施しています。採水直後にBACを最終濃度0.1%で添加し、48時間以内にSterivex(0.45 μm)でろ過しました。ろ過後に RNAlater 2 mL を添加して -20°C で保存し、陰性対照として蒸留水1 Lを同様に処理しています。
抽出は Wong et al. (2020) の手順に従い、RNAlater 除去後に PBS/Buffer AL/Proteinase K で 56°C 30分溶解、エタノール添加後にDNeasyで精製し、150 μLで溶出しました。
Wong et al. (2020) の解説記事はこちら
PCRとライブラリ調製
比較したプライマーは以下の2系統です。
| Primer name | Forward | Reverse | Remark |
|---|---|---|---|
| MtInsects-16S | 5′-GGACGAGAAGACCCTWTAGA-3′ | 5′-ATCCAACATCGAGGTCGCAA-3′ | 16S rRNA、183–252 bp |
| fwhF2 + EPTDr2n | 5′-GGDACWGGWTGAACWGTWTAYCCHCC-3′ | 5′-CAAACAAATARDGGTATTCGDTY-3′ | COI、約142 bp |
MtInsects-16S のライブラリ調製は2 step PCRです。
1st PCRは15 μL反応を4反復で実施し、35サイクル (98°C 10 s、55°C 5 s、68°C 5 s) で増幅しました。4反復分をプールして0.6×–0.8×のサイズ選択を行い、2nd PCRは10サイクル (98°C 10 s、60°C 5 s、68°C 5 s) でインデックス付与を実施しています。fwhF2 + EPTDr2n 側は Leese et al. (2021) のプロトコルに従っています。
シーケンスと解析パイプライン
シーケンスは MiSeq (2×300 bp) で実施し、MtInsects-16S は Bioengineering Lab、COI側は IDEA Consultants に委託しています。
解析はDemultiplex (サンプルごとにデータ配分) 後にペアの結合を行い、低品質塩基 (Phred Q<20 ?) や不一致の多いリード (>5 bp または <90%一致) を除外しました。期待エラー <1.0、対象領域長を 16Sで >180 bp、COIで >140 bp を条件にフィルタリングし、プライマー除去後にユニーク配列集計・エラー/キメラ除去を実施しています。
リード数が8倍以上異なる近縁配列は小さい方をエラーとして除去し、読み取り数 <7 の配列も削除しました。
ZOTUに >97% でマッピングして各サンプルのリード数を確定し、ネガティブコントロールのリード数は差し引いて補正しています。サンプル間の比較では最小リード数に合わせて rarefaction(希釈化) を行いました。
分類同定は県DB + GenBank を併用し、16Sでは 門レベル(e-value 1e−40) 、 目レベル(e-value 1e−60、identity >90%、query cover >90%) 、 種レベル(identity >98%、query cover >98%) の3段階、COIでは種レベルのみを用いて判定しました。DB間で同定結果が食い違う場合は無効扱いとし、属止まりの配列(“sp.”)や判別不能な近縁群は統合して扱っています。DB未登録種は NoDB として扱われます。
環境要因と群集解析
環境要因はGISで評価し、標高(5m DEM)、Strahler stream order(1/25,000地形図)、河床勾配(10 m標高差の距離から算出)を算出しています。群集構造はpresence/absenceデータの Jaccard距離にもとづく階層クラスタリング(hcluster, vegan)で解析し、手法間のサイト類似性を比較しています。
Results
検出率と手法間の重複
採集で確認された種の検出率は MtInsects-16S が 74.9%、COI一般マーカーが 40.1% で、併用では 80.0% に改善しました。
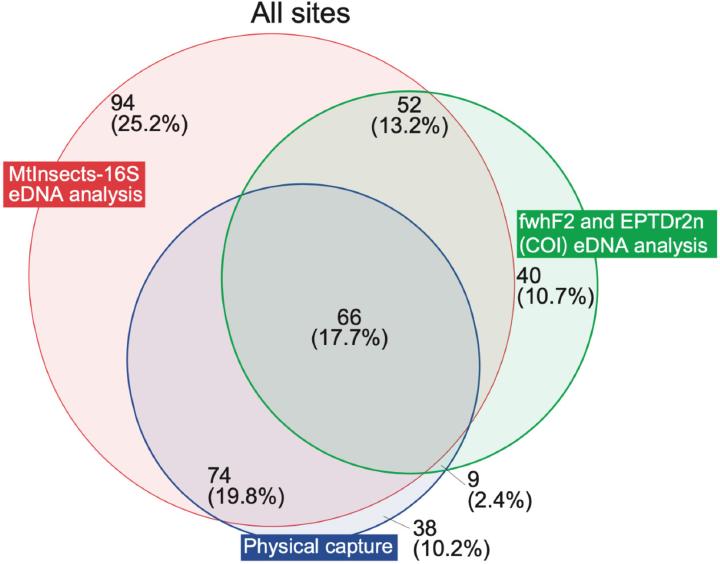
Fig. 3 は全地点の検出分類群の重複を示しています。MtInsects-16Sのみで検出された分類群は94 (25.2%)、COIのみは40 (10.7%)、3プライマー共通は66 (17.7%) で、16Sが採集に近い一方でCOI固有の拾い上げもある という関係が読み取れます。
検出分類
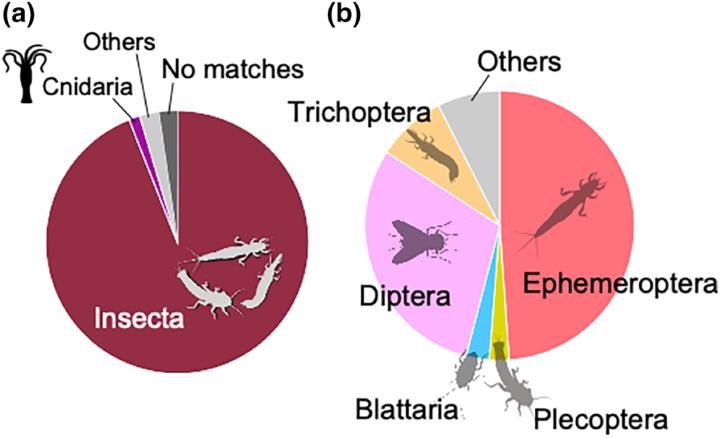
MtInsects-16S で検出された分類群の内訳は Insecta が大部分 を占めます(Fig. 2a)。Insecta内では カゲロウ目(Ephemeroptera) が最大割合で、 ハエ目(Diptera) 、 トビケラ目(Trichoptera) 、 カワゲラ目(Plecoptera) が続きます(Fig. 2b)。EPT群が中心に検出される点は、水質評価との相性が良い結果です。
調査地点間の類似性
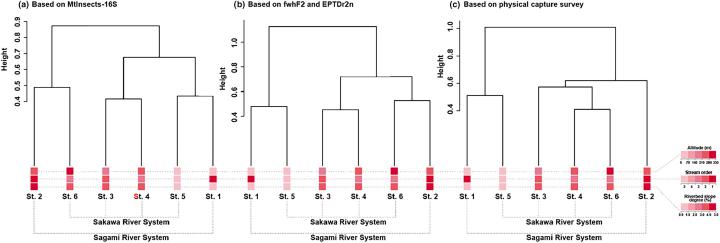
Fig. 4 は、各サイトの群集組成の類似性を階層クラスタリングで示しています。16S/COI/採集のいずれでも St.3–St.4、St.1–St.5、St.2–St.6 が近く、サイト間の相対関係が概ね再現されています。
標高・Stream order・河床勾配の類似性と群集組成の近さが対応している可能性が示唆されます。
結果の解釈や意義
本研究の意義は、単に「16Sが良かった」という結論にとどまりません。DB整備とプライマー選択をセットで考える必要性を、定量的に示した点が大きいといえます。環境DNA調査はコストと時間の制約が大きいため、現場ではしばしば「とりあえず一般マーカーでやる」という選択がされがちです。しかし、その場合、対象分類群に対する参照DBの薄さや非標的増幅の影響で、検出率が大きく落ちるリスクがあります。
MtInsects-16S は水生昆虫専用に設計されているため、COI一般マーカーと比べて昆虫に対する特異性が高く、非標的の増幅が抑えられることが期待されます。今回の結果はその期待を裏付けるものであり、実河川でのモニタリングにおいても実用的であることを示しています。実務的には、16Sを主軸にしつつCOIを補助的に併用し、参照DBを継続的に更新するという運用が最も合理的で、再現性の高い長期モニタリングに向きます。
研究の限界と今後の課題
一方で、いくつかの課題も残ります。第一に、地域特化DBは有効ですが、地域外での汎用性が担保されるわけではない点です。別地域で同様の精度を得るためには、その地域の参照DB整備が必要となります。第二に、環境DNAの検出は採水タイミングや水文条件に影響されるため、採集との一致率は季節や流況で変動し得ます。今回の成果は「適切に整備されたDBと最適化されたプライマーがあれば、高い検出率を得られる」という条件付きの結論だと理解するのが妥当です。
さらに、COI一般マーカーは他分類群との比較や既存DBとの互換性が強みであり、完全に代替されるべきものではありません。むしろ、用途に応じて16SとCOIを使い分ける、あるいは併用するという戦略が現実的です。今回、併用で検出率が80%に上がった点は、運用設計のヒントとして重要です。
まとめ
本研究は、水生昆虫の環境DNAメタバーコーディングにおいて、MtInsects-16S がCOI一般マーカーより高い検出率を示すことを、実河川データと採集比較で示しました。加えて、参照DBの整備が検出性能を左右する決定的要因であることを明確にしています。水生昆虫の長期モニタリングを現場で実装するためには、プライマー選択と参照DB整備を一体で考える必要があるというメッセージを強く示した論文です。
免責事項
十分注意は払っていますが、本記事の情報・内容について保証されるものではありません。また、本記事の利用や閲覧によって生じたいかなる障害についても責任を負いません。そして、本記事の情報は予告なく変更される場合がありますので、ご理解くださいますようにお願い申し上げます。